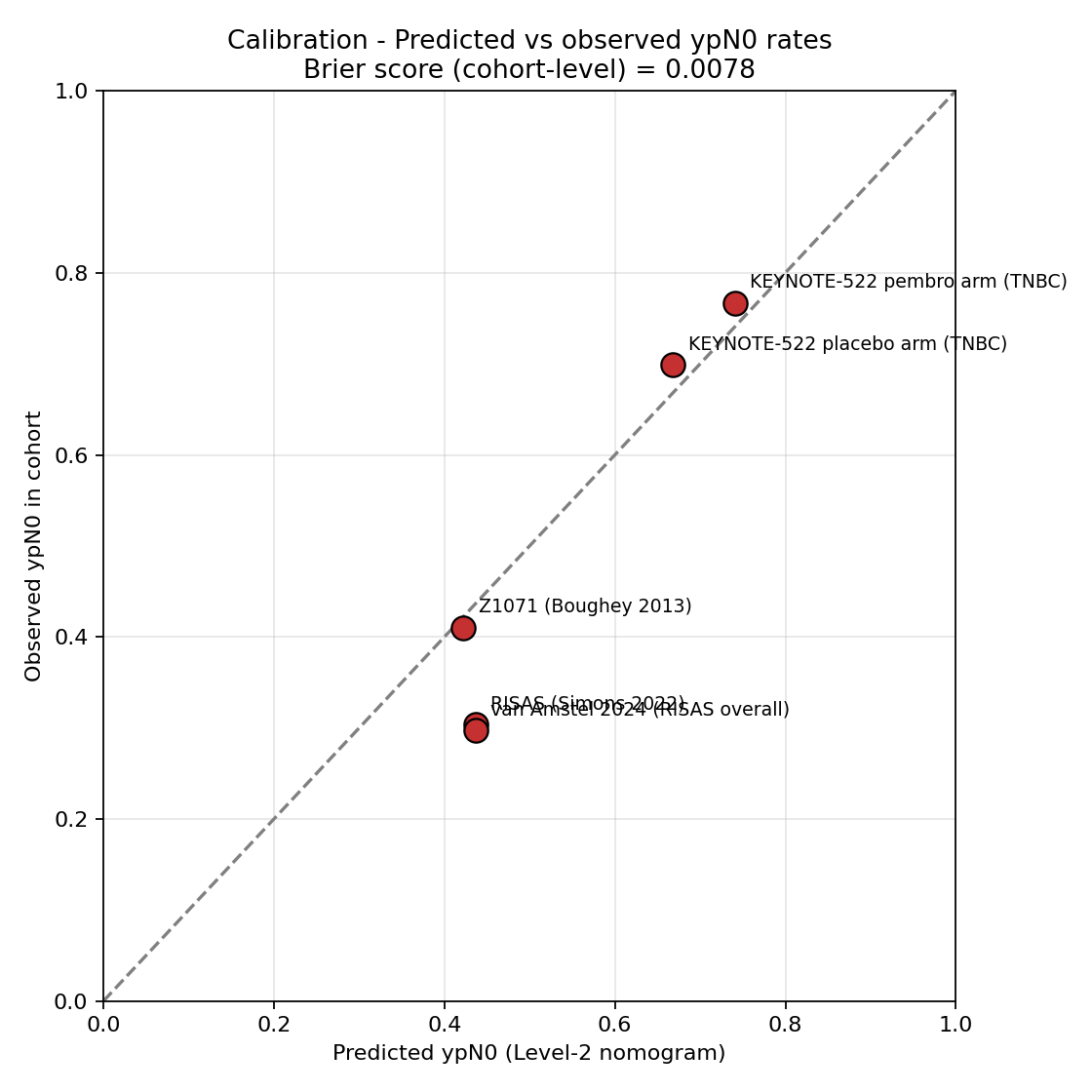
Tasas pooled de ypN0 por subtipo molecular
Forest plot de proporciones combinadas con DerSimonian–Laird. La diferencia clínica clave: HR-/HER2+ alcanza ypN0 en ~2 de cada 3 pacientes; HR+/HER2- apenas en ~1 de cada 5.
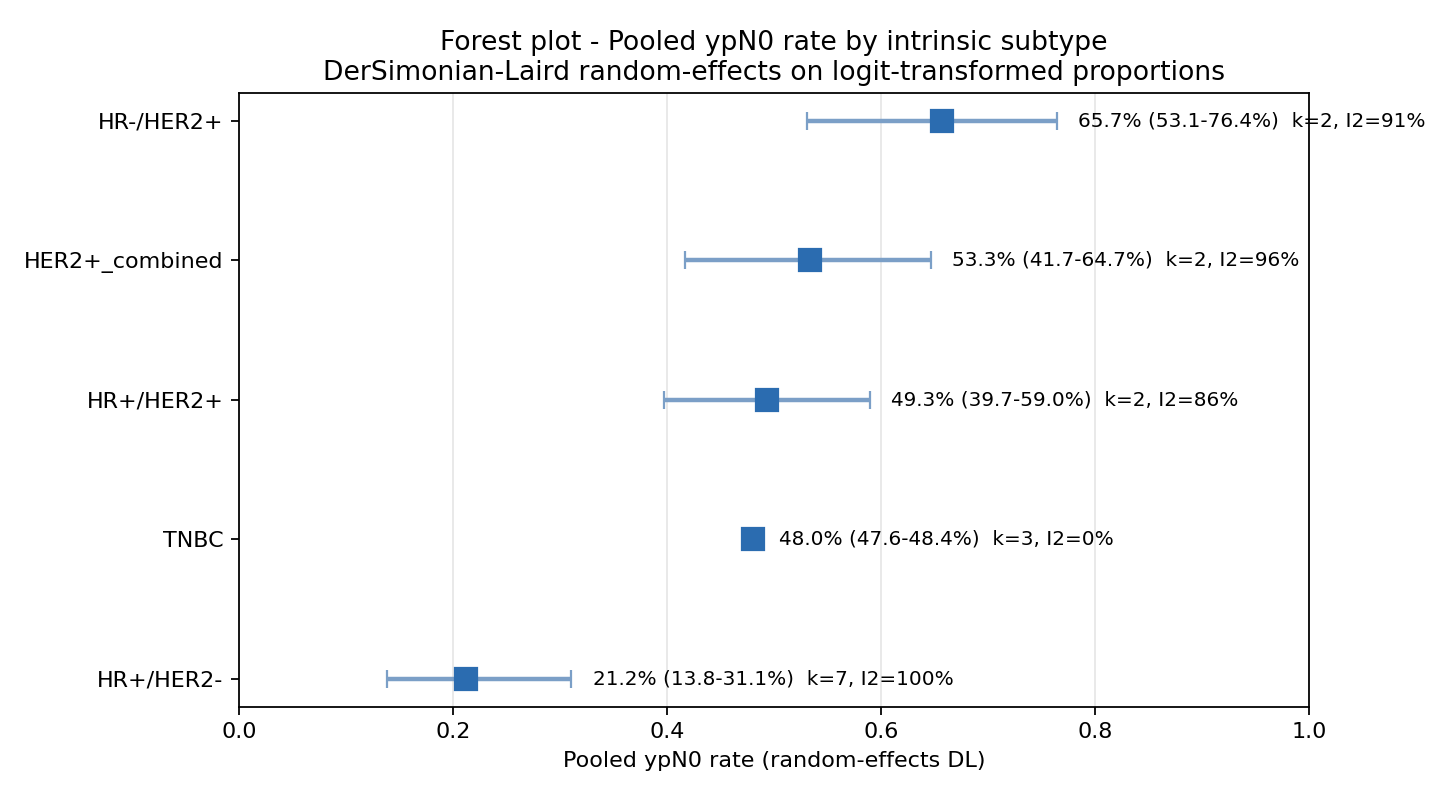
| Subtipo | k estudios | N total | Tasa pooled | IC 95% | I² |
|---|---|---|---|---|---|
| HR-/HER2+ | 2 | 57,716 | 65.7% | 53.1 – 76.4 | 90.7% |
| HR+/HER2+ | 2 | 57,716 | 49.3% | 39.7 – 59.0 | 86.4% |
| HER2+ (combinado) | 2 | 57,947 | 53.3% | 41.7 – 64.7 | 95.8% |
| TNBC | 3 | 58,132 | 48.0% | 47.6 – 48.4 | 0.0% |
| HR+/HER2- | 7 | 173,758 | 21.2% | 13.8 – 31.1 | 99.9% |
Lectura clínica. HR-/HER2+ es el subtipo con mayor desescalada axilar potencial post-NAT (~65%); HR+/HER2- el menos respondedor (~21%). La I² alta refleja heterogeneidad inter-estudio real (mezcla de cN1 vs cN2-3, modernidad del régimen, era pembrolizumab/pertuzumab), no error de extracción.